Playlist
Show Playlist
Hide Playlist
BRCA2 Gene
-
Slides 15 Genomics ComparativeGenomeAnalysis Genetics.pdf
-
Reference List Molecular and Cell Biology.pdf
-
Download Lecture Overview
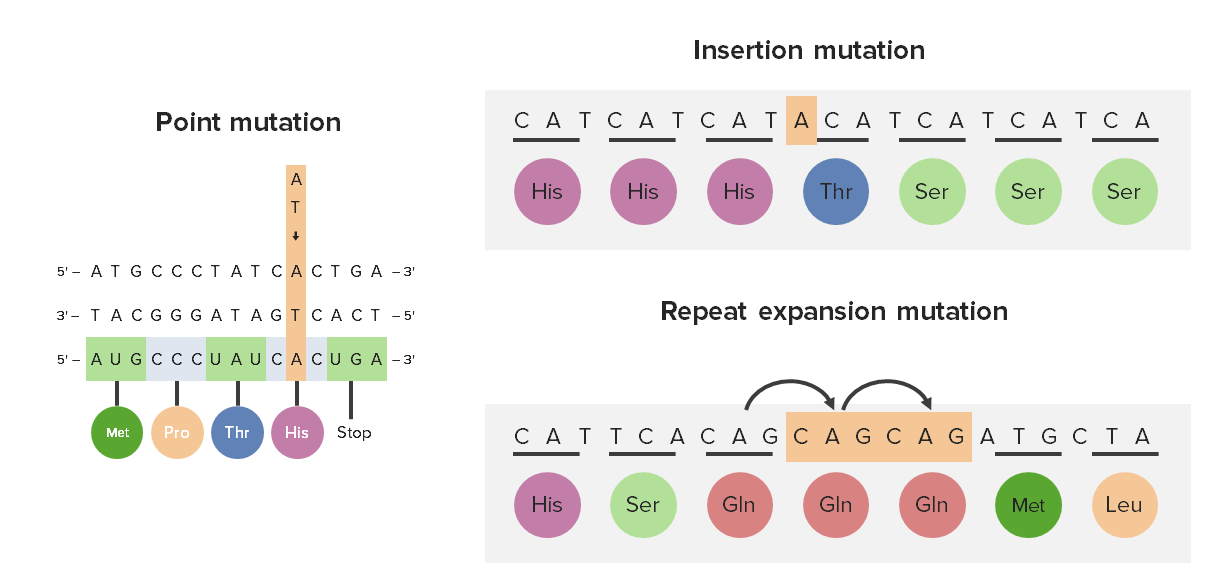
00:00 Und wir werden uns die Haplotypen hier gleich in Aktion sehen. Hier ist unser BRCA2-Gen. 00:03 Dies ist auf hapmap.org zu sehen. HapMap ist eine der Datenbanken, in die Forscher ihre Informationen über Einzelnukleotid-Polymorphismen, die sie in verschiedenen Populationen identifiziert haben und mit bestimmten Genfunktionen verbunden sind, stellen. Man sieht hier einen sehr kleinen Locus auf einem Chromosom für das BRCA2-Gen, dargestellt durch den vertikalen gelben Streifen oben in der sehr schmalen Region. 00:33 Und wir können das auf eine längere Region ausdehnen und jetzt sehen wir uns das gelbe Band an. 00:39 Hier sehen Sie die erweiterte Version aller Einzelnukleotid-Polymorphismen. Mehr als Sie dachten, ja. Es gibt eine Menge Forschungsprojekte, die sich mit einzelnen Nukleotidenpolymorphismen an all diesen verschiedenen Loci befassen. Hier, zum Beispiel, nehmen wir nun einen, der leicht zu erkennen ist. Wir sehen uns diesen C-Locus an, wir könnten also C oder T an diesem Locus haben. Und wenn wir C oder T haben, könnten wir verschiedene Phänotypen sehen. Schauen wir mal, was passiert, wenn wir buchstäblich auf diesen Locus klicken. Wir können sehen, dass eine Studie auftaucht, die die Häufigkeit des C gegenüber der Häufigkeit des T und der spezifischen Populationen, in denen an diesem Locus geforscht wurde, darstellt. Wirklich ziemlich cooles Zeug. Ich empfehle Ihnen, sich auf die Suche auf HapMap oder einer der anderen Datenbankseiten für einen einzelnen Nukleotid-Polymorphismus zu machen und zu sehen, ob Sie sich einen Reim darauf machen können. 01:47 Sie können auch eindeutig sehen, dass es Exons und Introns gibt, auf dem gelben Band unten markiert. Die Introns werden nicht exprimiert. Die Exons werden exprimiert, aber es ist nicht egal, ob es sich um ein Intron oder ein Exon sind, denndie so genannten Einzelnukleotid-Polymorphismen sind nur dazu da, um mit Genen in Verbindung zu treten. Schauen wir uns an, wie das funktioniert. 02:12 Diese genomweiten Assoziationsstudien verwenden Einzelnukleotid-Polymorphismen zur Identifizierung spezifischer Mutationen. Sie sind nicht die Mutation selbst, aber sie sind oft nahe an der Mutation, so dass es sehr unwahrscheinlich ist, dass ein Crossing-Over-Ereignis zwischen den Einzelnukleotid-Polymorphismus und dem eigentlichen Gen von Interesse stattfindet. Sie sind sehr nahe beieinander. 02:42 Je näher sie beieinander liegen, desto unwahrscheinlicher, dass sie sich kreuzen, denn sie sind so nahe, wie sie es kaum je sein könnten. Es ist in den Milliarden einer Möglichkeit, dass es eine Überschneidung mit einem dazwischen liegenden Ereignis haben könnte. Das heißt, im Wesentlichen liegen der Einzelnukleotid-Polymorphismus und das Merkmal sehr nahe beieinander. Zum Beispiel, hier können wir den SNP-Locus sehen, und man könnte C oder das T in diesem Locus haben, sehr nahe beieinander, aber nicht im Gen. Wir können sehen, ob diese Person ein hohes oder niedriges Risiko hat, laut der genomweiten Assoziationsstudie entspricht vielleicht C der Hochrisikoversion des Allels und T ist die Version mit dem geringeren Risiko und so können wir testen, ob jemand dieses Gen mit dem hohen Risiko hat und ob somit ein hohes Risiko für Brustkrebs besteht. 03:39 Ich weiß nicht, ob es wirklich das C oder das T ist, dies ist nur ein Beispiel. Stellen Sie keine Diagnosen damit. Wie auch immer, ist es nicht großartig, wie wir sehen können, wie Gene mit Hilfe von Einzelnukleotid-Polymorphismen erkannt werden?
About the Lecture
The lecture BRCA2 Gene by Georgina Cornwall, PhD is from the course Genomics.
Included Quiz Questions
Which of the following is a reason that single nucleotide polymorphisms (SNPs) are a good way to identify a phenotype?
- They are so close to the actual gene that it is very unlikely that a crossing-over event would remove the SNP.
- There is no chance that SNPs will ever have a mutation event.
- They are always the same nucleotide.
- They always repeat multiple times before the start codon.
- SNPs follow a triplet CTT pattern such that you always know where to look.
Customer reviews
5,0 of 5 stars
| 5 Stars |
|
5 |
| 4 Stars |
|
0 |
| 3 Stars |
|
0 |
| 2 Stars |
|
0 |
| 1 Star |
|
0 |