Playlist
Show Playlist
Hide Playlist
Coding and Noncoding DNA Sequences
-
Slides 15 Genomics ComparativeGenomeAnalysis Genetics.pdf
-
Reference List Molecular and Cell Biology.pdf
-
Download Lecture Overview
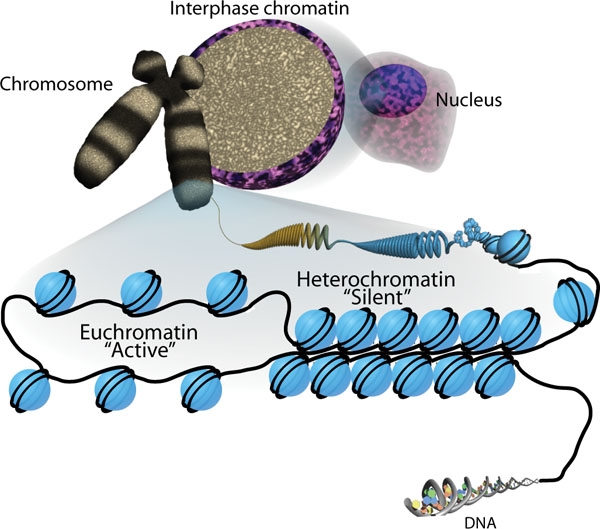
00:00 Das ist ein tolle Erklärung, aber es muss noch etwas anderes vor sich gehen. Wenn wir uns die DNA ansehen, dann kann ich Ihnen sagen, dass wir einige ziemlich konsistente Muster erkennen. Es gibt kodierende Regionen und nicht kodierende Regionen. Die Arten von DNA, die wir in kodierende Regionen finden, sind Gene mit nur einer Kopie. Diese sind Gene, die eine Funktion haben. 00:24 Wir können auch sehen, dass es segmentale Duplikationen gibt. Eine segmentalen Duplikation ist zum Beispiel, dass eine gesamte Sequenz der kodierenden Gene auf ein anderes Chromosom übertragen werden. Chromosom 16, zum Beispiel, hat eine hohe Prävalenz im gesamten Genom. Abschnitte vom Chromosom 16 werden, ich glaube auf 19 verschiedene Chromosomen, übertragen. 00:51 Darüber hinaus können wir kodierende Regionen sehen, die eine Multigenfamilie haben. Gene, die zusammenarbeiten, sich an ähnlichen Stellen auf dem Chromosom befinden oder in der Sequence, so dass sie zusammen produziert werden können, wenn wir diesen Abschnitt der DNA entschlüsseln. Und dann können wir ein Tandemcluster haben. Diese Tandemcluster sind Gene, die in mit einer hohen Rate repliziert werden müssen. 01:18 Es ist ein Cluster von Genen. Nehmen wir mal an, dass wir einen ganzen Haufen der gleichen Art eines Proteins auf einmal hergestellt haben möchten. Das Gen wird oft wiederholt, damit das Protein in einem grossen Volumen produziert werden kann. Wenn wir diese Region übersetzen und Transkription, müssen wir mehrere Kopien zur gleichen Zeit transkribieren, weil es mehrere Kopien von Gene in einer Reihe gibt. Das sind unsere kodierenden DNA-Sequenzen. Aber noch interessanter sind die nicht-kodierenden DNA-Sequenzen. Wir haben sehr viel Zeit damit in der Forschung verbracht und haben versucht zu charakterisieren, was in diesen nicht-kodierenden Sequenzen vor sich geht. Das sind die, die wir zuvor Junk-DNA genannt haben. Nun, wir wissen jetzt, dass es definitiv keine Junk-DNA ist. Wenn man sie "wegwirft", laufen einige Dinge überhaupt nicht gut. Zunächst einmal wissen wir, dass es Exons gibt. Ich meine, es gibt Introns und Exons. Die Exons werden exprimiert. Die Introns werden nicht exprimiert. Also, in nicht kodierende Regionen haben wir Introns. Dann haben wir strukturelle DNA - zum Beispiel um die Zentromere von Chromosomen. Diese DNA scheint keine Funktion zu haben , aber sie bleibt eng gewickelt, so dass die Zentromere eine Struktur haben, an der die die Kinetochor-Griffe sich befestigen können. Die Struktur DNA kodiert nicht. Wir haben einfache Sequenzwiederholungen. Wir haben sie gesehen, als wir uns den DNA-Fingerabdruck mit STRs angesehen haben, kurzen Tandem-Wiederholungen. Einfache Sequenzwiederholungen, die für nichts kodieren. Wir benutzen sie für Dinge, aber was sind ihre Aufgaben? Nachforschungen sind auf dem Weg, um diese Dinge herauszufinden. Wir können auch sehen, dass es segmentale Duplikationen gibt. 03:05 Dies sind große Regionen von Chromosomen, die verschoben und in andere Regionen kopiert werden, ähnlich wie bei der Kodierungsabschnitten, aber es sind keine Kodierungsabschnitte. Warum bewegen sich diese Abschnitte? Das bringt uns auf die Idee der transponierbaren Elemente. 03:21 Transponierbare Elemente sind auch als springende Gene bekannt. Sie sind überall im Genom zu finden und sie können sich selbst von einem Ort zum anderen bewegen. Wir haben uns lange gefragt, was der Zweck dieser springenden Gene sind. Wir können auch Pseudogene sehen. 03:40 Das sind Gene, die vielleicht durch ein springendes transponierbares Element inaktiviert wurden. 03:46 Oder sie sind mutiert, so dass sie keine funktionelle Expression mehr haben. 03:55 Wir kennen auch nicht codierende Abschnitte von Mikro RNAs. Diese bilden kleine Baby-RNAs, die vielleicht auch an der Genexpression beteiligt sind, sowie lange nicht-kodierende RNAs.
About the Lecture
The lecture Coding and Noncoding DNA Sequences by Georgina Cornwall, PhD is from the course Genomics.
Included Quiz Questions
Which of the following is NOT correctly associated?
- Introns – a part of a gene that is expressed in a mature mRNA molecule
- Pseudogene – a nonfunctional gene that originates due to the insertion of a transposon element or a mutation
- Simple sequence repeats – helpful in DNA fingerprinting
- Centromeric DNA – a structural part of centromeres that helps in proper segregation and the transport of chromosomes during cell division
- Transposon – a jumping gene that can change its position within the genome
Which of the following does NOT belong to the coding DNA sequences?
- Transposon
- Single copy gene
- Multigene families
- Tandem clusters
Customer reviews
5,0 of 5 stars
| 5 Stars |
|
5 |
| 4 Stars |
|
0 |
| 3 Stars |
|
0 |
| 2 Stars |
|
0 |
| 1 Star |
|
0 |